Software zur Bekämpfung der COVID-19-Pandemie – Wikipedia
Zur Bekämpfung der COVID-19-Pandemie wurden verschiedene Arten von Software entwickelt und eingesetzt. Dazu gehören mobile Apps für die Kontaktpersonennachverfolgung und Benachrichtigungen über Infektionsrisiken, digitale Pässe, die Impfstatus verifizieren, Desktop-Software zur Ermöglichung oder Verbesserung der Wirksamkeit von Lockdowns und räumlicher Distanzierung im Allgemeinen, Web-Software zur Erstellung von Informationsdiensten, sowie Software für die Forschung und Entwicklung zur Bekämpfung der COVID-19-Pandemie.
Kontaktverfolgung
[Bearbeiten | Quelltext bearbeiten]
COVID-19-Apps zur Kontaktverfolgung sind Apps für Mobilgeräte um den Infektionsschutz technisch zu unterstützen.
Design
[Bearbeiten | Quelltext bearbeiten]Es wurden viele verschiedene Apps zur Kontaktverfolgung entwickelt. Design-Entscheidungen, z. B. in Bezug auf die Privatsphäre der Benutzer, variieren zwischen den Apps. In den meisten Fällen sind die verschiedenen Apps nicht interoperabel, was ihre Effektivität beeinträchtigen kann, wenn mehrere Apps innerhalb eines Landes verwendet werden oder über Landesgrenzen hinweg gereist wird. Es wurde vorgeschlagen, dass die Entwicklung einer einzigen Open-Source-App (oder einer kleinen Anzahl solcher), die von allen genutzt werden kann, Interoperabilität gewährleistet und für die, mit dem Ziel einer robusten und optimalen App, Arbeitskraft gebündelt und kombiniert wird, einer solchen hochgradig parallelen Entwicklung vorzuziehen gewesen wäre.[1][2]
Nutzung und Wirksamkeit
[Bearbeiten | Quelltext bearbeiten]Eine unangereizte und stets völlig freiwillige Nutzung solcher Apps zur digitalen Kontaktverfolgung durch die Öffentlichkeit wurde als gering eingestuft,[3][4][5] selbst wenn die Apps so gebaut sind, dass die Privatsphäre gewahrt bleibt. Ein Mangel an möglichen Funktionen und weit verbreitete Fehler reduzieren ihren Nutzen weiter.[6] Die Nutzung einer solchen App im Allgemeinen oder zu bestimmten Zeiten ist in vielen oder allen Fällen nicht nachweisbar.
Check-in-Funktionalität
[Bearbeiten | Quelltext bearbeiten]Einige Apps erlauben auch „Check-Ins“, die eine Kontaktverfolgung und Risikobenachrichtigung nach Betreten von öffentlichen Orten wie Fitnessstudios ermöglichen.[7]
Digitaler Impfpass und Immunitätsausweis
[Bearbeiten | Quelltext bearbeiten]Ein digitaler Impfnachweis ist Software zur Verifizierung des Impfstatus einer Person.[4] Gleichermaßen würden digitale Immunitätsausweise eine hohe Wahrscheinlichkeit der Immunität – etwa durch Vorerkrankung oder Impfung – bescheinigen.[8]
Solche Pässe können es geimpften Personen ermöglichen, Zugang zu Veranstaltungen, Gebäuden und Dienstleistungen in der Öffentlichkeit zu erhalten, wie z. B. Flugzeuge, Konzertorte und Fitnessstudios,[4] und Lockerungen bzw. Öffnungen ermöglichen.[9]
Hürden und ethische Implikationen
[Bearbeiten | Quelltext bearbeiten]COVID-19-Impfstoffe werden in der Regel auf der Grundlage von Infektionsrisiken verteilt, wobei die Gewährung von Privilegien auf der Grundlage der Zertifizierung des Impfstatus einige ethische Implikationen hat –[9] so wie auch alle anderen Mechanismen/Faktoren, durch die die Gesellschaft Individuen Privilegien zuordnet. Zum Beispiel können Privilegien, die auf dem Impfstatus basieren, dazu führen, dass Menschen, die kein hohes Risiko für eine COVID-19-Infektion oder eine schwere Prognose der Krankheit haben, einen großen Teil des begrenzten Vorrats an Impfdosen erhalten (über die Gesellschaftsmechanismen der Finanz) und den geimpften Menschen Genehmigungen erteilt werden, die von ungeimpften Menschen als „unfair“ angesehen werden könnten. Außerdem könnten solche Pässe eine fälschungssichere, die Privatsphäre respektierende, überprüfbare, sichere digitale Zertifizierungstechnologie erfordern.
Design
[Bearbeiten | Quelltext bearbeiten]Mehrere Gruppen haben erklärt, dass gemeinsame Standards wichtig sind. Da es keine zügigen adäquaten technischen Mechanismen für ihr gemeinsames Design – oder die Etablierung eines festen Konsenses dafür – gibt, entwickeln einige Teams multi-kompatible Lösungen.[4]
Die COVID-19-Credentials-Initiative, die von der Linux Foundation Public Health (LFPH) organisiert wird, ist eine globale Initiative, die daran arbeitet, datenschutzfreundliche, fälschungssichere und überprüfbare Credential-Zertifizierungsprojekte auf der Grundlage des offenen Standards Verifiable Credentials (VCs) zu entwickeln und einzusetzen.[10][11]
Laurin Weissinger argumentiert, dass es wichtig ist, dass solche Software vollständig frei und quelloffen ist, dass die Konzepte und Entwürfe rechtzeitig erläutert werden, dass sie von Sicherheitsexperten penetrationsgetestet wird und dass kommuniziert wird, welche und wie Daten gesammelt und verarbeitet werden, da dies notwendig ist, um das erforderliche Vertrauen aufzubauen.[12] Jenny Wanger, Director of Programs bei der Linux Foundation, behauptet ebenfalls, dass es wichtig ist, dass solche Software open source ist.[13]
Webseiten
[Bearbeiten | Quelltext bearbeiten]
Web-Software wurde eingesetzt, um die Öffentlichkeit über den neuesten Stand der Pandemie zu informieren. Das Wiki Wikipedia[14][15] und COVID-19-Dashboards[16][17] wurden häufig genutzt, um aggregierte, integrierte und zuverlässige Informationen über die Pandemie zu erhalten. Darüber hinaus haben Bürger eine Vielzahl von Websites konsultiert, um proaktiv in Erfahrung zu bringen, welche Aktivitäten zum jeweiligen Zeitpunkt und Region erlaubt oder verboten sind – beispielsweise wann nächtliche Ausgangssperren gültig sind.
Medizinische Software
[Bearbeiten | Quelltext bearbeiten]GNU Health
[Bearbeiten | Quelltext bearbeiten]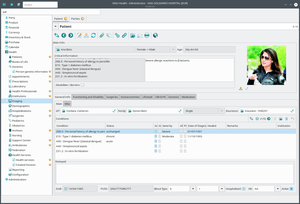
Die freie, Qt und GTK-basierte, Software GNU Health hat eine Vielzahl von Standardfunktionen, die sie während einer Pandemie nützlich machen.[17] Da die Software Open Source ist, ermöglicht sie vielen verschiedenen Parteien die gemeinsame Arbeit an einem einzigen integrierten Programm – anstelle von verschiedenen Programmen für verschiedene Zwecke und verschiedenen Programmen für verschiedene Nutzer pro Zweck, um die Nützlichkeit während der Pandemie zu erhöhen und es an ihre Bedürfnisse anzupassen. Zu den bereits vorhandenen Funktionen gehören eine Möglichkeit, die klinischen Informationen über die eindeutige „Person Universal ID“ automatisch in jeder Gesundheitseinrichtung sofort verfügbar zu machen oder diese zu aktualisieren, Vorlagen und Funktionen für Labortestberichte, Funktionen für die digitale Signierung und Verschlüsselung von Daten sowie die Speicherung von Krankenakten. Theoretisch könnte die Software verwendet oder modifiziert werden, um z. B. COVID-19-Tests und die Forschung über COVID-19 zu unterstützen, da durch den sicheren Austausch von anonymisierten Patientendaten und individuellen Ergebnissen – auch durch Hausärzte – die Forschung zum Virus und klinische Studien beschleunigt werden kann. Die Software wurde als mögliches Rückgrat einer robusten, nachhaltigen und auf Kooperation basierenden Infrastruktur für das öffentliche Gesundheitswesen in Betracht gezogen.[18]
Software für COVID-19-Tests
[Bearbeiten | Quelltext bearbeiten]In Bayern wurde eine Verzögerung bei der Übermittlung von 44.000 Testergebnissen durch die fehlende Nutzung oder vorbereitende Einrichtung oder Entwicklung der erforderlichen Software verursacht.[19]
Impfmanagement
[Bearbeiten | Quelltext bearbeiten]Software wird eingesetzt, um die Verteilung der kühl zu haltenden Impfstoffe zu managen und zu erfassen, welche Personen bereits eine – und welche – Impfung erhalten haben. Die fehlende Nutzung bzw. vorbereitende Einrichtung oder Entwicklung der benötigten Software führte laut Berichten zu Verzögerungen und anderen Problemen.[20]
Nextstrain
[Bearbeiten | Quelltext bearbeiten]
Nextstrain[21] ist seit 2015 online, eine Zusammenarbeit zwischen Forschern in Seattle (USA) und Basel (Schweiz).[22] Nextstrain ist eine Open-Source-Plattform für genomische Daten von Krankheitserregern für Epidemiologen, Virologen, Beschäftigte des Gesundheitssektors und die Bevölkerung. Nextstrain enthält eine Datenbank, eine Bioinformatik-Analyse und eine interaktive Echtzeit-Visualisierungsplattform für Mutationen und Virusvarianten.[23] Neben dem Dengue-Fieber, Grippe, Masern, Mumps, Tuberkulose, West Afrika Ebola, West-Nil-Virus und Zika wird hier auch die virale Evolution von SARS-CoV-2 analysiert und dargestellt.[21] Während der COVID-19-Pandemie wird die Plattform extensiv für die Erforschung neuer Varianten von SARS-CoV-2 genutzt.[24]
Modellierungs-Software
[Bearbeiten | Quelltext bearbeiten]Es wurden wissenschaftliche Software-Modelle und -Simulationen für SARS-CoV-2 genutzt – etwa zur Verbreitung,[25] Funktionsmechanismen und Eigenschaften,[26][27][25] Wirksamkeit potenzieller Behandlungen,[27][25] Übertragungsrisiken und Impfmodellierung/Überwachung. (Numerische Strömungsmechanik, computergestützte Epidemiologie …)
Modellierungssoftware und verwandte Software wird auch dazu verwendet, die Auswirkungen auf die Umwelt (siehe #Webseiten) und die Wirtschaft abzuschätzen.
Ergebnisse aus solchen Modellen werden in der wissenschaftsbasierten Politikgestaltung und der Entwicklung von Behandlungsmethoden verwendet.[25]
Folding@home
[Bearbeiten | Quelltext bearbeiten]
Im März 2020 erreichte das Volunteering-basierte Distributed-Computing-Projekt Folding@home als erstes System der Welt einen ExaFLOPS.[28][29][30] Das System simuliert Proteinfaltung, wurde für die medizinische Forschung auf COVID-19 eingesetzt und erreichte am 13. April 2020 eine Geschwindigkeit von ca. 2,43 x86 exaFLOPS – ein Vielfaches des bis dato schnellsten Supercomputers Summit.[31]
COVID-19-Forschung zum Repurposing von Medikamenten
[Bearbeiten | Quelltext bearbeiten]Supercomputer – darunter die weltweit leistungsfähigsten Einzel-Supercomputersysteme Summit und Fugaku – wurden in Versuchen eingesetzt, potenzielle Behandlungen zu identifizieren, indem Simulationen mit Daten zu bestehenden, bereits zugelassenen Medikamenten durchgeführt wurden.[32][33][34][25][27]
Siehe auch
[Bearbeiten | Quelltext bearbeiten]- Technologiepolitik
- Gruppenarbeit (Arbeitsorganisation)
- Informationsmanagement
- Digitale Einreiseanmeldung, DEMIS, SORMAS
- Pandemieprävention#Überwachung und Kartierung
- Epidemiologische Überwachung
Einzelnachweise
[Bearbeiten | Quelltext bearbeiten]- ↑ Ramsey Faragher: We Are Losing Sight Of What Contact Tracing Apps Are For. In: Forbes. Abgerufen am 8. April 2021 (englisch).
- ↑ Robert Ranisch, Niels Nijsingh, Angela Ballantyne, Anne van Bergen, Alena Buyx, Orsolya Friedrich, Tereza Hendl, Georg Marckmann, Christian Munthe, Verina Wild: Digital contact tracing and exposure notification: ethical guidance for trustworthy pandemic management. In: Ethics and Information Technology. 21. Oktober 2020, ISSN 1572-8439, doi:10.1007/s10676-020-09566-8 (englisch, springer.com).
- ↑ Deutsche Welle (www.dw.com): Too few Germans using coronavirus pandemic tracing app | DW | 17.09.2020. In: DW.COM. Abgerufen am 8. April 2021.
- ↑ a b c d Vaccine passport apps are here. But the technical challenges are still coming. In: The Seattle Times. Abgerufen am 8. April 2021
- ↑ 96% of Canadians who test positive for coronavirus aren’t using COVID Alert app properly. In: Global News. Abgerufen am 8. April 2021.
- ↑ Corona-Warn-App 2.0: Check-in per QR-Code startet nach Ostern. In: t3n Magazin. Abgerufen am 8. April 2021.
- ↑ Update der Corona-Warn-App: Anonym einchecken per QR-Code. In: tagesschau.de. Abgerufen am 8. April 2021.
- ↑ Corona-Immunitaetspass als App. Kommen digitale Impfpässe? In: www.br.de. Ehemals im (nicht mehr online verfügbar); abgerufen am 19. Februar 2023. (Seite nicht mehr abrufbar. Suche in Webarchiven)
- ↑ a b Government calls for input into Covid-19 vaccine passports In: ComputerWeekly.com. Abgerufen am 10. April 2021 (englisch).
- ↑ COVID-19 Credentials initiative : Home. In: www.covidcreds.org. Abgerufen am 8. April 2021.
- ↑ R. Dallon Adams in Innovation on February 8: Open source "vaccine passports:" Linux Foundation Public Health talks development, security, and digitally restoring trust. In: TechRepublic. Abgerufen am 8. April 2021 (englisch).
- ↑ Vaccination passport apps could help society reopen—if they are secure, private and trusted. In: phys.org. Abgerufen am 8. April 2021 (englisch).
- ↑ Tariro Mzezewa: Coming Soon: The ‘Vaccine Passport’. In: The New York Times. 4. Februar 2021, abgerufen am 8. April 2021.
- ↑ Shaan Sachdev: Wikipedia’s Sprawling, Awe-Inspiring Coverage of the Pandemic In: The New Republic, 26. Februar 2021. Abgerufen am 27. Februar 2021
- ↑ Noam Cohen: How Wikipedia Prevents the Spread of Coronavirus Misinformation. In: Wired. 15. März 2020 (wired.com).
- ↑ NASA COVID-19 Dashboards Give a View of the Virus’s Effects from Above | NASA Applied Sciences. In: appliedsciences.nasa.gov. Abgerufen am 8. April 2021 (englisch).
- ↑ a b An introduction to GNU Health Embedded — Free Software Foundation — Working together for free software. In: www.fsf.org. Abgerufen am 8. April 2021.
- ↑ Luis Falcón: Tackling the beast: Using GNU Health to help the fight against the | Joinup. In: joinup.ec.europa.eu. 9. April 2020, abgerufen am 8. April 2021 (englisch).
- ↑ German coronavirus tests backlog: 900 positive not yet told In: ABC News. Abgerufen am 9. April 2021 (englisch).
- ↑ COVID-19 vaccine rollout may be delayed - with IT system 'failing constantly' In: Sky News. Abgerufen am 9. April 2021 (englisch).
- ↑ a b Nextstrain-maintained pathogen analyses. nextstrain.org, abgerufen am 4. September 2021 (englisch).
- ↑ Universität Basel: Corona-Pandemie: Mit Nextstrain dem Virus auf der Spur. unibas.ch, 20. März 2021, abgerufen am 4. September 2021: „Dass Richard Neher heute so gefragt ist, liegt auch daran, dass er und sein Kollege Trevor Bedford vom Fred-Hutchinson-Krebsforschungszentrum in Seattle schon vor Jahren eine innovative Idee hatten. Sie wollten live mitverfolgen können, wie sich Krankheitserreger ausbreiten und haben eigens dafür die Webapplikation Nextstrain entwickelt. Seit 2015 ist die Webseite online“
- ↑ James Hadfield et al.: Nextstrain: real-time tracking of pathogen evolution. In: Bioinformatics. oup.com, 1. Dezember 2018, abgerufen am 4. September 2021 (englisch, Bioinformatics, Volume 34, Issue 23, Pages 4121–4123). doi:10.1093/bioinformatics/bty407
- ↑ WHO: Tracking SARS-CoV-2 variants. In: Activities. who.int, 31. August 2021, abgerufen am 3. September 2021 (englisch).
- ↑ a b c d e Supercomputers, giant accelerators lend a hand in the fight against coronavirus In: University of Chicago News. Abgerufen am 10. April 2021 (englisch).
- ↑ UChicago chemists race to decode RNA of new coronavirus In: University of Chicago News. Abgerufen am 10. April 2021 (englisch).
- ↑ a b c Ellen Gray: NASA Supercomputers Power COVID-19 Research In: NASA, 28. Mai 2020. Abgerufen am 10. April 2021 (englisch).
- ↑ Folding@Home Crushes Exascale Barrier, Now Faster Than Dozens of Supercomputers - ExtremeTech In: www.extremetech.com. Abgerufen am 13. Mai 2020
- ↑ Folding@home crowdsourced computing project passes 1 million downloads amid coronavirus research In: VentureBeat, 31. März 2020. Abgerufen am 13. Mai 2020
- ↑ The coronavirus pandemic turned Folding@Home into an exaFLOP supercomputer In: Ars Technica, 14. April 2020. Abgerufen am 13. Mai 2020 (amerikanisches Englisch).
- ↑ Liam Tung: CERN throws 10,000 CPU cores at Folding@home coronavirus simulation project In: ZDNet. Abgerufen am 13. Mai 2020 (englisch).
- ↑ San Diego supercomputer uncovers several potential COVID-19 treatments In: KGTV, 6. Januar 2021. Abgerufen am 10. April 2021 (englisch).
- ↑ Japanese supercomputer finds 30 existing drugs potentially effective to treat COVID-19 In: Mainichi Daily News, 4. Juli 2020. Abgerufen am 10. April 2021 (englisch).
- ↑ World's fastest supercomputer finds 77 potential COVID-19 treatments In: Futurism. Abgerufen am 10. April 2021 (englisch).


 French
French Deutsch
Deutsch